En extrapolant la dynamique actuelle des données hospitalières, une saturation des services de réa/soins intensifs est à craindre courant novembre (cf. précédents tweets). Quand réagir, et avec quelle intensité ? Explorons ici les médianes de deux scénarios extrêmes. Thread 1/4
A) Scénario de contrôle léger mais précoce : une baisse du taux de transmission à un niveau comparable à celui du mois de juin doit être apportée au plus tard mi-octobre pour rester sous 5000 lits de réanimation occupés par des patients COVID (capacité pré-épidémique). 2/4 

B) Scénario de contrôle tardif mais lourd : une baisse du taux de transmission à un niveau comparable à celui du confinement doit être apportée au plus tard mi-novembre pour rester sous la barre des 12000 patients COVID en réanimation (capacité étendue). 3/4 
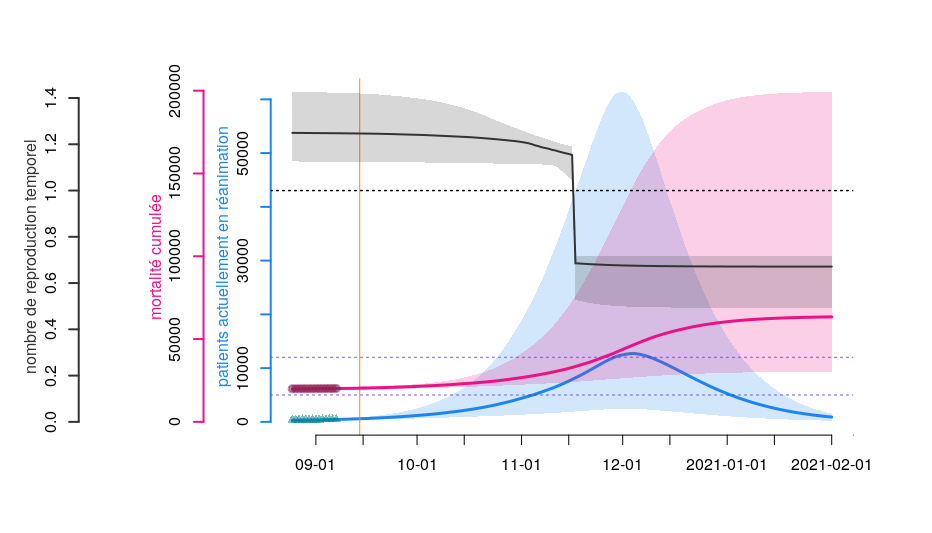
En résumé, plus vite l'épidémie est contrôlée, moins le coût des restrictions est important. Plus les mesures sont prises tard, plus les conséquences sont dramatiques et plus il est difficile de tenir compte des dynamiques locales. 4/4 @threadreaderapp
unroll
unroll
• • •
Missing some Tweet in this thread? You can try to
force a refresh